Uzun Kodlamayan RNA Çalışmalarında Gözden Kaçan DNA Sinyali Yöntemleri Yanıltıyor
Uzun kodlamayan RNA’lar (lncRNA), protein üretmemelerine rağmen gen ifadesini yöneten karmaşık ağlarda kritik roller üstleniyor. Son yıllarda bu moleküllerin kromatinle nasıl etkileştiğini anlamaya yönelik ilgi hızla arttı; ChIRP-seq, CHART-seq ve RAP-seq gibi yüksek verimli dizileme teknikleri de bu alanın temel araçları haline geldi. Ancak bu yöntemlerle çoğu zaman binlerce bağlanma bölgesi rapor edilmesi, lncRNA’ların hücre içindeki görece düşük bolluğuyla her zaman uyumlu görünmüyordu. Nature Biotechnology’de yayımlanan yeni çalışma, tam da bu tutarsızlığın ardında önemli bir teknik kaynak olabileceğini ortaya koyuyor: DNA’nın oligonükleotid problarla beklenmedik biçimde eşleşmesi sonucu oluşan “DNA off-targeting” etkisi.
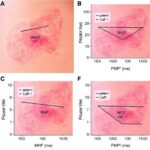
Goldrich, Delhaye, Bekaert ve çalışma arkadaşlarının yürüttüğü analiz, insan ve fare hücrelerinden elde edilmiş RNA-kromatin etkileşim verilerinin kapsamlı bir meta-analizine dayanıyor. Araştırmacılar, özellikle NESPR adlı belirli bir lncRNA’ya odaklanarak bu transkriptin farklı endojen ifade düzeylerine sahip hücre hatlarındaki kromatin etkileşim profilini yeniden değerlendirdi. Elde edilen bulgular, daha önce RNA’ya atfedilen birçok bağlanma olayının gerçekten biyolojik bir temas yerine, kullanılan problarla kısmi tamamlayıcılık gösteren DNA parçalarının yakalanmasından kaynaklanabileceğini düşündürüyor. Bu sonuç, lncRNA-kromatin haritalamasında yıllardır kullanılan veri kümelerinin bir bölümünün ihtiyatla yorumlanması gerektiğine işaret ediyor.
Çalışmanın önemi yalnızca tek bir RNA’ya ilişkin yeni bir yorum sunmasından ibaret değil. Araştırma, lncRNA’ların genom üzerindeki konumlarını belirlemek için tasarlanan yakalama temelli yöntemlerde ortak bir zafiyete dikkat çekiyor. ChIRP-seq, CHART-seq ve RAP-seq gibi teknikler, belirli RNA dizilerine tamamlayıcı oligonükleotidler kullanarak RNA ile ilişkili kromatin parçalarını çekip ayırmaya dayanıyor. Bu yaklaşım güçlü olmakla birlikte, hedef RNA yerine benzer diziler taşıyan DNA fragmanlarının da yakalanabilmesi teknik bir risk oluşturuyor. Yeni çalışmada incelenen sinyallerin bir kısmı, işte bu tür istenmeyen çekimlerin sonucu olarak değerlendirildi.
Bilim insanlarının asıl kaygısı, bu tür artefaktların lncRNA araştırmalarında aşırı yorumlara yol açabilmesi. Bir lncRNA için binlerce bağlanma bölgesi bildirilmesi, yüzeyde bu molekülün genom genelinde son derece yaygın bir düzenleyici gibi görünmesine neden olabilir. Oysa gerçek biyolojik etkileşimlerin sayısı, teknik gürültü ayıklandığında çok daha sınırlı olabilir. Bu durum, lncRNA’ların işlevini anlamaya çalışan araştırmalar için yalnızca niceliksel değil, kavramsal bir sorun da yaratıyor; çünkü bağlanma haritaları çoğu zaman bir RNA’nın hangi genleri ya da hangi kromatin bölgelerini etkileyebileceğine dair en güçlü kanıt olarak kabul ediliyor.
Çalışmada dikkat çeken bir diğer nokta, hücresel ifade düzeyinin yorumlamadaki rolü oldu. Bir lncRNA’nın az ya da çok üretilmesi, onun gerçekten hangi kromatin bölgelerine temas ettiğini anlamada önemli bir ayırt edici olabilir. Ancak DNA off-targeting gibi teknik etkiler, bu ilişkiyi bulanıklaştırarak düşük bolluktaki RNA’larda dahi yapay olarak zenginleşmiş sinyaller üretebilir. Araştırmacılar, bazı bölgelerde gözlenen bağlanma sinyallerinin RNA’nın biyolojik davranışıyla değil, prob tasarımının belirli DNA dizilerine istemeden yakın olmasıyla açıklanabileceğini gösterdi. Bu, özellikle veri tabanlarında yer alan büyük ölçekli lncRNA etkileşim haritalarının yeniden gözden geçirilmesini gerektirebilir.

 Nöronların Başlangıç Noktasında Beklenmedik Uyarıcı Bağlantılar Keşfedildi
Nöronların Başlangıç Noktasında Beklenmedik Uyarıcı Bağlantılar Keşfedildi
 Yaşlanan Tümör Ortamında Gizli Mekanizma: Meme Kanserini Daha Saldırgan Yapan RAGE Sinyali
Yaşlanan Tümör Ortamında Gizli Mekanizma: Meme Kanserini Daha Saldırgan Yapan RAGE Sinyali
 Isı Temelli Tedavi, İlaç Dirençli Epilepside Beyin Ağlarını Yeniden Düzenliyor
Isı Temelli Tedavi, İlaç Dirençli Epilepside Beyin Ağlarını Yeniden Düzenliyor