Tek Moleküllük Okuma: A*STAR’dan RNA’nın Katlanma Kodunu Çözmeye Yönelik Yeni Yöntem
Singapur’daki A*STAR Genome Institute of Singapore (ASTAR GIS) araştırmacıları, RNA’nın yalnızca dizisini değil, aynı zamanda tek tek moleküller üzerindeki üç boyutlu davranışını da inceleyebilen yeni bir yöntem geliştirdi. sm-PORE-cupine adı verilen bu yaklaşım, RNA’nın hücre içindeki işlevini belirleyen katlanma desenlerini daha önce mümkün olandan daha ayrıntılı biçimde görünür kılıyor. Bulgular, gen regülasyonunu anlamada yeni bir pencere açarken, hastalıkların moleküler düzeyde çözümlenmesi ve gelecekte RNA odaklı tedavilerin geliştirilmesi açısından da dikkat çekiyor.
RNA uzun süre yalnızca DNA’dan gelen genetik bilgiyi taşıyan bir ara molekül olarak tanımlandı. Ancak son yıllarda bu bakış açısı önemli ölçüde değişti. RNA’nın, DNA’daki çift sarmala kıyasla çok daha esnek bir yapıya sahip olduğu ve farklı ikincil ile üçüncül katlanma biçimleri alarak hücresel süreçleri düzenleyebildiği artık biliniyor. Bu katlanmalar, proteinin ne kadar verimli üretileceğini, RNA’nın hücre içinde ne kadar süre kalacağını ve hangi moleküllerle etkileşeceğini etkileyebiliyor. Bu nedenle RNA yapısı, gen ifadesinin ince ayarında kritik bir rol oynuyor.
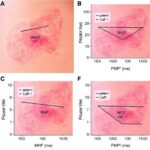
Ancak RNA’nın bu esnekliği, aynı zamanda onu incelemeyi son derece zorlaştırıyor. Mevcut yapısal analiz yöntemlerinin çoğu, tek bir RNA molekülünü izlemek yerine çok sayıda molekülden gelen sinyalleri birleştiriyor. Bu da belirli bir RNA dizisi için ortalama bir tablo sunuyor, fakat aynı genin ürünleri arasında ortaya çıkabilen küçük ama işlevsel farklılıkları gizleyebiliyor. Özellikle aynı RNA dizisinin farklı hücre koşullarında ya da farklı zamanlarda değişen katlanma biçimlerini anlamak, bu ortalama yaklaşım nedeniyle güçleşiyor. Araştırmacılara göre, tam da bu boşluk RNA biyolojisinde uzun süredir çözülmeyi bekleyen temel sorunlardan biri olarak öne çıkıyordu.
sm-PORE-cupine, bu sorunu aşmak için sitelere özgü kimyasal işaretleme ile nanopore tabanlı doğrudan RNA okumasını bir araya getiriyor. Bu birleşik tasarım, bilim insanlarının tek bir RNA molekülünün tamamını incelemesine ve işaretlenen bölgelerin yapısal bağlamını doğrudan değerlendirmesine olanak tanıyor. Böylece yöntem, yalnızca RNA’nın hangi bazlardan oluştuğunu değil, hangi bölgelerinin erişilebilir, hangilerinin ise katlanma nedeniyle gizlenmiş olduğunu da ortaya çıkarabiliyor. Teknik, adından da anlaşılacağı üzere, molekül düzeyinde “okuma” ile yapısal bilgi üretmeyi aynı platformda buluşturuyor.
Bu tür bir yaklaşımın önemi, RNA’nın işlevinin çoğu zaman diziden çok katlanma düzeniyle belirlenmesinden kaynaklanıyor. Aynı RNA dizisi, hücre içinde farklı şekiller alarak farklı biyolojik sonuçlar doğurabiliyor. Örneğin bazı yapısal motifler protein sentezini yavaşlatabilir, bazıları RNA’yı yıkımdan koruyabilir, bazıları ise hücresel proteinlerle etkileşimi kolaylaştırabilir. Dolayısıyla RNA yapısındaki küçük değişimler bile gen regülasyonunda büyük etkiler yaratabiliyor. Tek molekül seviyesinde yapı analizi yapılabilmesi, bu değişimlerin neden ve nasıl ortaya çıktığını incelemek için güçlü bir araç sunuyor.
Yeni yöntemin bilimsel değeri, özellikle heterojenliğin anlaşılmasında öne çıkıyor. Bir hücre popülasyonunda aynı RNA dizisi, tamamen aynı davranmak zorunda değil. Aynı transkript farklı katlanma durumları arasında gidip gelebilir ve bu durumların her biri farklı bir biyolojik sonuç doğurabilir. Toplu analizler bu çeşitliliği ortalamaya gömdüğü için, işlevsel açıdan önemli alt gruplar gözden kaçabilir. sm-PORE-cupine ise bu varyasyonu görünür hale getirerek RNA yapısının dinamik doğasını daha gerçekçi bir çerçevede değerlendirme imkânı veriyor.
Bu gelişme, temel biyoloji açısından olduğu kadar hastalık araştırmaları açısından da önemli. RNA yapısındaki bozulmaların bazı genlerin yanlış düzenlenmesine katkıda bulunabileceği, bunun da çeşitli hastalık süreçleriyle ilişkili olabileceği uzun zamandır bilinen bir olasılık. Ayrıca viral RNA’lar da konak hücre içinde benzer yapısal kurallara uyarak çoğalma ve bağışıklıktan kaçınma stratejileri geliştirebiliyor. Bu nedenle RNA’nın tek molekül düzeyinde yapısal haritalanması, yalnızca insan genlerinin değil, virüslerin RNA mekanizmalarının da daha iyi anlaşılmasına yardımcı olabilir.
Araştırmanın doğrudan sonuçları henüz erken aşamada değerlendirilse de, böyle bir teknolojinin ilaç geliştirme çalışmalarında da değerli olması bekleniyor. RNA hedefli tedaviler ve RNA yapısına bağlanan küçük moleküller üzerine çalışan alanlar, hedefin hangi yapısal durumda bulunduğunu bilmeye giderek daha fazla ihtiyaç duyuyor. Bir RNA’nın sabit değil, farklı katlanma halleri arasında geçiş yapan bir molekül olduğu düşünüldüğünde, tek bir “ortalama” yapıya göre tasarlanan stratejiler yetersiz kalabiliyor. Bu yüzden tek moleküllük yapısal analiz, daha seçici ve mekanizmaya dayalı tasarımlar için önemli bir temel sağlayabilir.
A*STAR GIS ekibinin sm-PORE-cupine ile sunduğu yenilik, RNA biyolojisinde ölçüm kapasitesini bir adım öteye taşıyor. Yöntem, RNA’nın yalnızca genetik mesajı taşıyan bir ara ürün değil, yapısı aracılığıyla hücresel kararları yönlendiren dinamik bir molekül olduğunu daha net gösteriyor. Bilim insanları için bundan sonraki asıl soru, bu yapısal çeşitliliğin farklı hastalık bağlamlarında nasıl değiştiği ve hangi durumlarda müdahale edilebilir hale geldiği olacak. Yeni teknik, bu sorulara daha ayrıntılı yanıtlar verebilecek araçlardan biri olarak öne çıkıyor.

 Plastik Kaynaklı BPA’nın Sperm Hasarına Karşı Paraprobiotik Umut: OMU Araştırmasından Yeni Bulgular
Plastik Kaynaklı BPA’nın Sperm Hasarına Karşı Paraprobiotik Umut: OMU Araştırmasından Yeni Bulgular
 Yaşlı Kanser Hastalarında Dijital Sağlık Kaygısı Farklı Yüzler Gösteriyor
Yaşlı Kanser Hastalarında Dijital Sağlık Kaygısı Farklı Yüzler Gösteriyor
 CU Anschutz’ta Hızlandırılmış 3 Yıllık Tıp Eğitimi: Doktor Açığını Kapatma ve Öğrenci Yükünü Hafifletme Hamlesi
CU Anschutz’ta Hızlandırılmış 3 Yıllık Tıp Eğitimi: Doktor Açığını Kapatma ve Öğrenci Yükünü Hafifletme Hamlesi